Sette eccellenti risorse dati, strumenti software e pubblicazioni sottoposte a revisione tra pari dei nostri membri sono state riconosciute come SIB Remarkable Outputs , un appuntamento annuale dedicato all’eccellenza e alla diversità dei risultati ottenuti nel campo della bioinformatica in Svizzera.
Ti piacerebbe essere tra i risultati selezionati del prossimo anno? Visita la pagina Remarkable Outputs per conoscere la prossima scadenza per l'invio delle candidature.
-
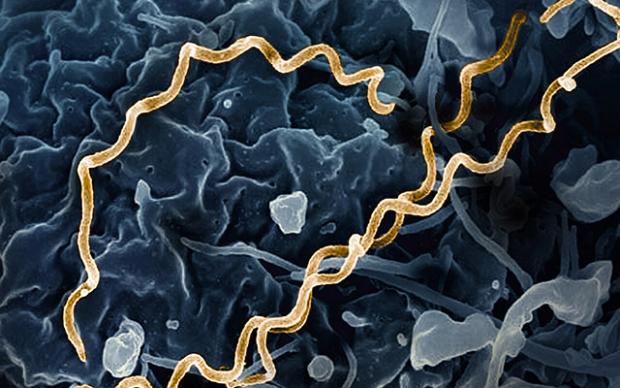
Uno strumento di ricerca rapida per sequenze biologiche
Pubblicato su: Nature
Gruppo SIB coinvolto: Informatica biomedica guidato da Gunnar Rätsch, presso l'ETH di Zurigo
Descrizione: MetaGraph individua in pochi secondi specifiche sequenze di DNA, RNA e proteine tra milioni di record pubblici. Come un normale motore di ricerca su Internet, questo strumento scalabile indicizza e interroga in modo efficiente enormi set di dati globali, stabilendo un nuovo standard per l’esplorazione su larga scala dei dati di sequenziamento.
Il commento della commissione: «MetaGraph affronta un importante collo di bottiglia: la capacità di cercare ed esplorare volumi di dati di sequenziamento in rapida crescita. Il suo eccezionale contributo tecnico trasforma il modo in cui gli scienziati esplorano i dati biologici su larga scala e accelera le scoperte in molti settori delle scienze della vita».
-
Uno strumento per valutare i complessi macromolecolari previsti dall'intelligenza artificiale
Pubblicato su: Nature Methods
Gruppo SIB coinvolto: Biologia strutturale computazionale guidato da Torsten Schwede, presso l'Università di Basilea
Descrizione: Nuovi strumenti di IA sono in grado di prevedere la struttura di grandi complessi biologici che coinvolgono proteine, DNA e piccole molecole. OpenStructure valuta l’accuratezza di tali previsioni confrontandole con strutture determinate sperimentalmente, attraverso un flusso di lavoro riproducibile, trasparente e scalabile.
Il parere della commissione: «OpenStructure rappresenta un importante passo avanti per la biologia strutturale e le pratiche di benchmarking, grazie alla creazione di un sistema robusto e completamente automatizzato per la valutazione dei metodi di previsione strutturale di nuova generazione basati sull’IA. Il sistema è già integrato nelle iniziative di benchmarking della comunità, a dimostrazione della sua rilevanza e del suo impatto».
-
Un metodo per rilevare gli effetti dell’origine genitoriale sui tratti
Pubblicato su: Nature
Il SIB coinvolto: Genetica statistica guidato da Zoltán Kutalik, presso l'Università di Losanna
Descrizione: È stato dimostrato cheil metabolismo , il rischio di malattia e altri tratti mutano in direzioni diverse — e persino opposte — a seconda che una variante genetica provenga dalla madre o dal padre. Lo studio ha utilizzato un approccio innovativo per analizzare gli effetti dell’origine parentale su ampi set di dati genetici umani.
Il parere della commissione: «Questo quadro analitico consente lo studio sistematico di un fenomeno evolutivo importante ma spesso trascurato. La capacità di dedurre l’origine parentale degli alleli con informazioni genealogiche limitate rappresenta un contributo significativo alla genetica statistica e alla bioinformatica».
-
Una banca dati sul microbioma intestinale a livello di sottospecie
Pubblicato su: Cell Host & Microbe
Il SIB coinvolto: Genomica evolutiva computazionale guidato da Evgeny Zdobnov ed Evgenia Kriventseva, presso l'Università di Ginevra
Descrizione: Il primo catalogo genomico completo dei microbi intestinali umani a livello di sottospecie rileva la variazione genetica all'interno della specie che le analisi standard non riescono a cogliere. I modelli di apprendimento automatico che utilizzano i profili di sottospecie HuMSub hanno previsto il cancro del colon-retto dai campioni di feci in modo più accurato rispetto ai modelli a livello di specie.
Il commento della commissione: «HuMSub affronta una limitazione di lunga data della ricerca sul microbioma. Distinguendo le sottospecie all’interno della stessa specie e collegando queste differenze a tratti funzionali e correlati alle malattie, l’approccio consente un’interpretazione biologica più precisa dei dati sul microbioma».
-
Uno strumento per lo studio dell'evoluzione basato sulle strutture proteiche tridimensionali
Pubblicato su: Nature Structural & Molecular Biology
Il SIB coinvolto: Genomica comparativa guidato dall' e Christophe Dessimoz, presso l'Università di Losanna
Descrizione: FoldTree svela le relazioni tra le proteine confrontando le loro strutture tridimensionali piuttosto che le loro sequenze genetiche. Questo approccio innovativo permette agli scienziati di tracciare antiche storie evolutive difficili da individuare utilizzando i metodi tradizionali basati sulle sequenze.
Il commento della commissione: «FoldTree dimostra come una svolta rivoluzionaria in un campo – in questo caso, la previsione della struttura proteica basata sull’intelligenza artificiale – possa aiutare ad affrontare una sfida di lunga data in un altro campo. La sua metodologia innovativa trova applicazione nella biologia strutturale, nella biologia evolutiva e in campi correlati».
-
Un metodo per la caratterizzazione genetica dei gruppi di cellule tumorali
Pubblicato su: Nature Genetics
Gruppo SIB coinvolto: Gruppo di Biologia Computazionale guidato da Niko Beerenwinkel, presso l'ETH di Zurigo
Descrizione: I gruppi di cellule tumorali presenti nel flusso sanguigno possono dare origine a metastasi. Un nuovo algoritmo consente l'analisi della sequenza del DNA delle singole cellule all'interno di tali cluster e fornisce la prima prova che molti di essi contengono cellule geneticamente distinte. Il metodo apre la strada a diagnosi meno invasive.
Il commento della commissione: «Risolvendo un problema complesso all’interfaccia tra filogenetica e genomica delle singole cellule, questo lavoro mette in evidenza il potere della bioinformatica nel promuovere le scoperte nella ricerca biomedica. Esemplifica inoltre il valore di una stretta collaborazione tra scienziati sperimentali e computazionali».
-
Uno strumento di intelligenza artificiale per una scoperta di farmaci più rapida ed economica
Pubblicato su: Nature
Gruppo SIB coinvolto: Laboratorio di Progettazione Proteica e Immunoingegneria guidato da Bruno Correia, presso l'EPFL
Descrizione: BindCraft progetta proteine "leganti" che modificano l'attività dei bersagli terapeutici in un unico passaggio computazionale, superando la necessità di uno screening sperimentale su larga scala. Lo strumento di IA open-source è già ampiamente utilizzato, con applicazioni comprovate che includono il blocco degli allergeni e il targeting preciso delle terapie geniche.
Il commento della commissione: «Questo metodo innovativo segna un significativo progresso per la progettazione delle proteine. Trasformando la scoperta dei leganti in un processo computazionale affidabile, apre nuove opportunità per la progettazione terapeutica e l’innovazione nel campo delle biotecnologie».






![Peer Bork giving a talk at the [BC]2 Basel Computational Biology Conference](/sites/default/files/styles/card_image/public/2026-01/Peer-Bork_banner.jpg?h=602a36b5&itok=KM0WZZWK)