Une équipe dirigée par Joana Pereira et Torsten Schwede au Biozentrum de l'Université de Bâle et au SIB a découvert un véritable trésor de protéines non caractérisées. Grâce à la récente révolution du deep learning et à une subvention Kickstarter du SIB, ils ont découvert des centaines de nouvelles familles de protéines, dont un nouveau repliement protéique. Cette étude a été publiée dans la revue Nature, en même temps qu'une autre étude du groupe SIB de Pedro Beltrao à l'ETH sur un sujet connexe.
Au cours des dernières années, AlphaFold a révolutionné la science des protéines. Cet outil d'intelligence artificielle (IA) a été entraîné à partir de données sur les protéines collectées par des scientifiques pendant plus de 50 ans et est capable de prédire la forme 3D des protéines avec une grande précision. Son succès a permis de modéliser pas moins de 215 millions de protéines l'année dernière, fournissant ainsi des informations sur la forme de presque toutes les protéines. Cela est particulièrement intéressant pour les protéines qui n'ont pas été étudiées expérimentalement, un processus complexe et chronophage.
« Il existe aujourd'hui de nombreuses sources d'informations sur les protéines, qui renferment des connaissances précieuses sur leur évolution et leur fonctionnement », explique Joana Pereira, responsable de l'étude. Néanmoins, la recherche est depuis longtemps confrontée à une jungle de données. L'équipe de recherche dirigée par Torsten Schwede, chef de groupe au Biozentrum de l'Université de Bâle, a maintenant réussi à décrypter certaines des informations cachées.
Une vue aérienne révèle de nouvelles familles et de nouveaux repliements de protéines
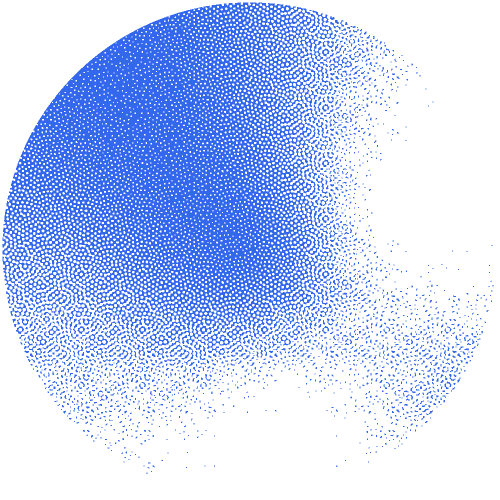
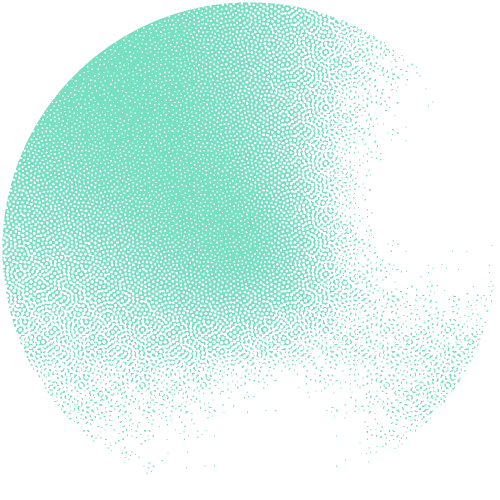
Les chercheurs ont construit un réseau interactif de 53 millions de protéines avec des structures AlphaFold de haute qualité. « Ce réseau constitue une source précieuse pour prédire théoriquement à grande échelle des familles de protéines inconnues et leurs fonctions », souligne Janani Durairaj, premier auteur. L'équipe a pu identifier 290 nouvelles familles de protéines et un nouveau repliement protéique qui ressemble à la forme d'une fleur.
S'appuyant sur l'expertise du groupe Schwede dans le développement et la maintenance du logiciel de pointe SWISS-MODEL, soutenu par le SIB, ils ont mis le réseau à disposition sous forme de ressource web interactive, baptisée « Protein Universe Atlas ».
En savoir plus sur notre portefeuille de logiciels et de bases de données de pointe
L'un des deux articles révolutionnaires publiés par les groupes SIB pour explorer la matière noire protéique
L'article décrit ici est l'un des deux articles publiés sur ce sujet par des groupes du SIB. En utilisant une approche complémentaire, basée sur la structure des protéines plutôt que sur leurs séquences, l'équipe de Pedro Beltrao à l'ETH Zurich et l'équipe de Martin Steinegger et de l'Université nationale de Séoul proposent une méthode efficace pour regrouper les protéines présentes dans la base de données AlphaFold. Leur principale conclusion a été de déterminer combien il existe de types de formes protéiques différentes, combien d'entre elles sont sous-étudiées et à quel moment de l'évolution elles ont pu apparaître. Les deux articles ont été mis en avant dans une interview publiée par Nature.
L'intelligence artificielle, un outil précieux pour la recherche
L'équipe a utilisé des outils basés sur l'apprentissage profond pour trouver des nouveautés dans ce réseau, ouvrant ainsi la voie à des innovations dans les sciences de la vie, de la recherche fondamentale à la recherche appliquée. « Comprendre la structure et la fonction des protéines est généralement l'une des premières étapes pour développer un nouveau médicament ou modifier leurs fonctions par génie protéique, par exemple », explique Pereira. Ce travail a été soutenu par une subvention « kickstarter » du SIB visant à encourager l'adoption de l'IA dans les ressources des sciences de la vie. Il souligne le potentiel transformateur de l'apprentissage profond et des algorithmes intelligents dans la recherche.
Grâce à l'Atlas de l'univers des protéines, les scientifiques peuvent désormais en savoir plus sur les protéines pertinentes pour leurs recherches. « Nous espérons que cette ressource aidera non seulement les chercheurs et les biocurateurs, mais aussi les étudiants et les enseignants en leur offrant une nouvelle plateforme pour découvrir la diversité des protéines, de leur structure à leur fonction en passant par leur évolution », déclare M. Durairaj.
Le réseau interactif est accessible gratuitement dans le monde entier ici.
Reference(s)
Durairaj J et al. Découverte de nouvelles familles et de nouveaux repliements dans l'univers des protéines naturelles. Nature. Publié en ligne le 13 septembre 2023.
Barrio-Hernandez I et al. Structures prédites par regroupement à l'échelle de l'univers protéique connu. Nature. Publié en ligne le 13 septembre 2023.